Vidal Rafael1, González Ana1, Gutiérrez Lucía2, Umaña Rodolfo1, Speranza Pablo1
1Departamento de Biología Vegetal, Facultad de Agronomía. UdelaR. Garzón 780. CP 12900.
Montevideo, Uruguay.
2Departamento de Biometría, Estadística y Computación, Facultad de Agronomía. UdelaR. Garzón 780. CP 12900. Montevideo, Uruguay. Correo electrónico: rvidal@fagro.edu.uy
]]>
Recibido: 16/12/09 Aceptado: 30/11/10
Resumen
Stipa neesiana es una gramínea forrajera invernal perenne de gran valor como recurso fitogenético en Uruguay. Para caracterizar la distribución de la diversidad genética y el sistema reproductivo de esta especie se utilizó la técnica de Random Amplified Polymorphic DNA (RAPD). Se seleccionaron cinco iniciadores que generaron 71 bandas de RAPD; se estudiaron 270 plantas de nueve poblaciones y siete progenies. Los resultados obtenidos muestran un porcentaje de autogamia cercano al 100%. Los parámetros heterocigosis esperada (He) y porcentaje de bandas polimórficas (P), evidenciaron una amplia variabilidad dentro de las poblaciones. El análisis de la diversidad genética entre las poblaciones estudiadas mediante el estimador del índice de fijación de Wright (FST) generó un valor de 0,44, lo que demuestra una significativa diferenciación genética entre las poblaciones. No se observó aislamiento por distancia, sin embargo las distancias genéticas entre poblaciones muestran una estructuración que se hizo evidente en los agrupamientos obtenidos.
]]>Palabras clave: ESTRUCTURA GENÉTICA, FORRAJERAS NATIVAS, MARCADORES MOLECULARES, RAPD, RECURSOS FITOGENÉTICOS
Summary
Distribution of genetic diversity and reproductive system of Stipa neesiana Trin. et Rupr.
Stipa neesiana is a cool-season perennial grass valued as an important genetic resource in Uruguay. Random Amplified Polymorphic DNA (RAPD) molecular markers were used in order to characterize the distribution of genetic diversity and breeding system in this species. Five primers were selected which generated 71 RAPD bands. Using these primers, 270 individuals from nine populations and seven progenies were studied. Our results show a selfing rate close to 100%. The parameters expected heterozygosity (He) and percentage of polymorphic bands (P), showed that considerable genetic variability can be found within populations. The study of genetic variability among populations as analyzed by the estimator of Wright’s fixation index (FST) yielded a value of 0.44 which shows that there is significant differentiation among populations. A pattern of isolation by distance was not observed; however, structuring in the genetic distances among populations can be observed in the groupings recovered.
Key words: GENETIC STRUCTURRE, NATIVE FORAGE GRASS, MOLECULAR MARKERS, RAPD, GENETIC RESOURCES
]]>
Introducción
El campo natural es una de las principales riquezas del Uruguay. Ocupa el 71% de la superficie útil, con más de 11 millones de hectáreas (DIEA, 2001). Es el recurso natural renovable que sustenta la producción ganadera y una pieza clave para la conservación de otros recursos como suelo, agua y fauna (Altesor et al., 2006). Presenta una gran abundancia de especies (Rosengurtt et al., 1939) y es allí donde ocurre la mayor diversidad de forrajeras nativas, el recurso fitogenético más importante del país (Berretta et al., 2007). La diversidad de especies se explica en parte por las variaciones en las características de topografía, propiedades físico químicas del suelo (Coughenour, 1991). En particular las diferentes formas de pastoreo de la ganadería pueden aumentar la diversidad del campo natural al evitar la predominancia de especies o disminuir la diversidad al homogeneizar áreas muy diversas donde las especies más palatables son más afectadas (Cingolani et al., 2008, Adler et al., 2001, Millot et al., 1987). Dentro de las forrajeras promisorias, Rosengurtt (1979) destaca gramíneas y leguminosas de los géneros Bromus, Paspalum, Stipa, Adesmia y Trifolium, entre otras. A la fecha se han realizado estudios de la diversidad genética de unas pocas especies en Uruguay (Speranza, 2005, Rivas, 2001), sin embargo hay muchas especies que no han sido estudiadas (Berretta et al., 2007).
Stipa neesiana Trin. & Rupr. 1842 (syn. Stipa setigera Presl. 1830; Nassella neesiana (Trin. & Rupr.) Barkworth), 2n = 2x = 28 (Bowden y Senn, 1962) es una gramínea cespitosa perenne invernal del campo natural. Originaria de América del Sur (Longhi-Wagner y Zanin, 1998) se encuentra en Uruguay en todo el territorio (Rosengurtt et al. 1970). Se ha reportado en Australia y Nueva Zelanda (Clayton et al., 2006) y en Islas Canarias e Islas Baleares (Wildpret de la Torre et al., 1999) como invasora. Esta especie es conocida por su fruto «flechilla» provisto de un apéndice punzante o callus, que favorece su diseminación (Izaguirre, 1993). Por ser una de las gramíneas invernales más frecuentes de nuestros campos y por sus buenas características productivas (Rosengurtt, 1979), se constituye en el principal aporte invernal a los rodeos de cría (Berreta et al.,1990). Su calidad y persistencia mejoran con cortes aliviados (Lacuague y Durán, 1989; Boggiano, 1990) así como pastoreos controlados y la fertilización nitrogenada pueden aumentar su macollaje y oferta forrajera (García et al., 2005). Esta especie resulta muy útil además en la regeneración de praderas naturales y para repoblar zonas erosionadas por su capacidad colonizadora (Burkart ,1969; Rosengurtt, 1946).
]]>El sistema reproductivo se considera como autógamo en base a observaciones morfológicas realizadas en esta especie, que ha sido descripta como cleistógama con espiguillas cleistógenas (Connor 1979, Rosengurtt et al., 1970, Rosengurtt, 1946). Si bien estas observaciones permiten considerar que la especie se reproduce principalmente por autogamia, no se han llevado a cabo estudios del sistema reproductivo efectivo de la especie. La proporción de fecundación cruzada que presenta una especie en condiciones naturales, puede ser determinada a través del análisis de los genotipos de familias de medios hermanos con marcadores genéticos codominantes o dominantes, con o sin control parental (Frankel y Galun, 1977, Ritland y Jain, 1981).
Respecto a la diversidad de Stipa neesiana, Arechavaleta (1894-97) y Burkart (1969) describen en conjunto cinco variedades para la especie en base a caracteres como volumen y pilosidad de nudos, ángulo de entrenudos, forma y pilosidad de hojas, tamaño y superficie de antecio y longitud de corona y aristas. Rosengurtt et al. (1970) mencionan para Uruguay las variedades neesiana y longiaristata. Arechavaleta (1894-97) basa esta diferenciación en la ausencia de pelos tanto en nudos como en hojas y en las dimensiones de las espiguillas y sus aristas («espiguillas grandes con aristas larguísimas»), mientras que Rosengurtt et al. (1970) definen esta variedad como aquellos ejemplares de la especie que poseen lemmas de base lisa y brillosa, sin hacer referencia al tamaño de la espiguilla ni al largo de sus aristas.
Las poblaciones naturales suelen mostrar diferencias en las frecuencias de alelos y genotipos de una región geográfica a otra. Esas estructuras geográficas en subpoblaciones pueden tener profundos efectos en la evolución de las especies (Hartl y Clark, 1997). Las diferenciaciones genéticas entre las poblaciones están afectadas por los sistemas reproductivos. En las autógamas la autopolinización aumenta los niveles de homocigosis y también incrementa la diversidad entre poblaciones (Hamrick y Godt,, 1990). El conocimiento de estas características de diversidad y estructura genética son claves para la valoración de las especies nativas como recurso fitogenético, y para desarrollar estrategias óptimas de muestreo, conservación y mejoramiento (Frankel et al., 1995).
]]>
A nivel morfológico, Rosengurtt et al. (1970) hacen referencia a una cierta zonificación en la distribución geográfica de la variedad longiaristata. Por otra parte, Symonds y Villagrán (1988), buscando descriptores morfológicos adecuados para la especie analizaron 34 variables. Estos autores encontraron que las diferencias entre poblaciones fueron mayores que dentro de poblaciones para todos los descriptores analizados, aunque el número de individuos estudiados por población fue bajo (10). Sólo se consideraron con mayor poder de discriminación ocho descriptores, de los cuales las variables: fecha de emergencia, largo y ancho de hoja, largo de panoja y ancho de fruto se correlacionaron con la distribución geográfica encontrándose fechas de emergencia más tempranas y dimensiones de fruto y hoja mayores en las poblaciones del norte del país respecto a los de poblaciones del sur. A pesar de esto, la información es fragmentaria y no existen resultados concluyentes.
Para diseñar adecuadamente estrategias de conservación y uso con resultados exitosos, es imprescindible conocer previamente la magnitud y distribución de la variabilidad genética de las especies a estudiar (Ramanatha Rao y Hodgkin, 2002). La información publicada indica que S. neesiana presenta mecanismos morfológicos que favorecen la autogamia y por lo tanto se espera que una proporción considerable de la variabilidad genética se encuentre distribuida entre poblaciones. El objetivo del presente trabajo es determinar el sistema reproductivo y cuantificar la variabilidad genética que existe entre y dentro de las poblaciones naturales de S. neesiana utilizando marcadores moleculares. Teniendo en cuenta lo fragmentario de la información y las inconsistencias entre los distintos autores, se tomará la especie como un todo.
Materiales y métodos
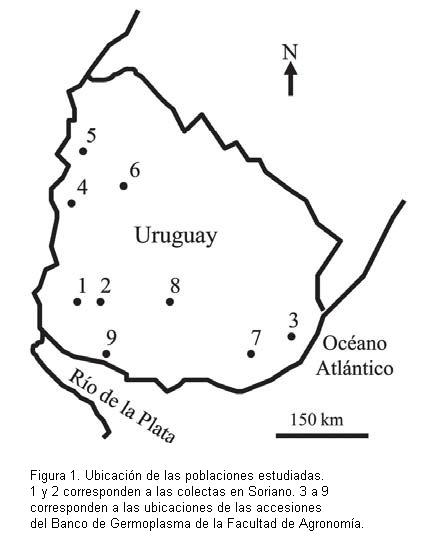
Para el estudio de diversidad se trabajó con dos poblaciones colectadas en el campo y siete regeneradas a partir de semillas conservadas en el Banco de Germoplasma de la Facultad de Agronomía. Las poblaciones colectadas (1 y 2) se encuentran en dos predios del departamento de Soriano, distantes entre sí 20 km. Se seleccionaron muestras de hojas de 30 plantas individuales por sitio. Las muestras fueron secadas y almacenadas en bolsas plásticas con gel de sílice para su traslado y conservación. Las poblaciones regeneradas (3 a 9) se escogieron por ser representativas de sitios diferentes y alejados entre sí dentro del Uruguay (Figura 1). Se regeneraron en invernáculo 30 individuos por población, las plántulas se transplantaron al jardín de la Facultad de Agronomía y de cada planta regenerada se colectó una hoja para la extracción de ADN. Para el estudio del sistema reproductivo se cosecharon semillas producidas en condiciones naturales por cinco individuos en su población de origen (Población 2). Las semillas fueron cosechadas en el mismo momento en que se muestrearon las plantas madres en el campo por lo que cada muestra consistió en la semilla presente en ese momento en cada individuo. La muestra se complementó con semillas de dos individuos pertenecientes a diferentes poblaciones regeneradas; en este caso las plantas madres estaban instaladas en una misma parcela junto con toda la colección de poblaciones regeneradas. Toda la semilla obtenida se utilizó para confeccionar germinadores y las plántulas resultantes fueron conservadas en invernáculo. Se analizó un total de 71 individuos para las siete progenies además de las siete plantas madres. El número de individuos recuperados por progenie varió entre tres y veinte. La extracción del ADN se realizó en el Laboratorio de Genética de la Facultad de Agronomía siguiendo un protocolo estándar CTAB-Cloroformo: Alcohol isoamílico (Doyle y Doyle, 1987). El ADN extraído fue cuantificado en un NanoDrop «Thermo Scientific 1000» mediante el análisis directo de un micro-volumen de muestra sin diluir, obteniendo la concentración de ADN en ng/uL y el valor del cociente entre la absorbancia a 260 y 280 nm.
Para la amplificación de ADN con iniciadores de RAPD (Williams et al. 1990) se utilizó una mezcla de reacción de 20 ml conteniendo alrededor de 120 ng de ADN con un cociente de absorbancia a 260/280 nm de aproximadamente 1,8. La mezcla de reacción consistió en concentraciones finales de 1,8 mM de MgCl2, 0,14 mM de dNTPs, 0,36 mM de iniciador, en el tampón provisto por el fabricante conteniendo 0,8 U de Taq ADN polimerasa. La amplificación se llevó a cabo en un termociclador «Thermo PX2» con las siguientes condiciones: una pre-desnaturalización de 5 min a 94 ºC, seguida de 40 ciclos de 94 ºC por 30s (desnaturalización), 35 ºC por 30s (hibridación), 72 ºC por 2 min (extensión) y 5 min a 72 ºC de extensión final. Los productos de amplificación fueron separados por electroforesis en geles de agarosa al 1,8% con tampón TBE 1X a 5 V/cm durante tres horas. Los geles se tiñeron con bromuro de etidio (0,5 mg/mL), se visualizaron bajo luz ultravioleta y fueron fotografiados digitalmente para su análisis posterior.
Las imágenes obtenidas fueron convertidas en matrices de presencia/ausencia con la ayuda del programa de análisis de imágenes Cross-Checker V 2.91 (Buntjer 2000) utilizando el criterio de que las bandas teñidas con similar intensidad en repetidas reacciones son las más predecibles (Heun y Helentjaris 1994). Para ello se estableció un umbral relativo en la intensidad de las bandas que se consideraron para confeccionar la matriz. Éste se estableció en base a los valores mínimos que presentaron las bandas que resultaron consistentes entre diferentes reacciones del mismo individuo con un mismo iniciador.
Análisis de datos
El análisis de reproducibilidad se realizó asignando valores de 1 para las bandas consistentes y de 0 para las inconsistentes en sucesivas repeticiones del mismo individuo con el mismo iniciador en distintas reacciones. El promedio obtenido para el total de individuos evaluados por iniciador refleja por lo tanto la proporción de bandas consideradas reproducibles con cada iniciador.
]]>El nivel de autofecundación se estimó calculando la tasa de alogamia para múltiples loci (tm) con el método de máxima verosimilitud implementado en el programa MLTR 3.2 (Ritland, 2002). Para evaluar el error estándar se tomaron 1000 muestras bootstrap.
La diversidad genética de las poblaciones se estimó con el número de loci polimórficos (P) como índice de riqueza genética y la heterocigosis esperada (He) como índice de diversidad. La He se estima bajo el supuesto de equilibrio utilizando la frecuencia de las ausencias para cada locus como la frecuencia del genotipo homocigoto recesivo, mientras que bajo el supuesto de homocigosis total la frecuencia de los fenotipos presencia y ausencia son iguales a las frecuencias de los alelos correspondientes. Las evaluaciones se realizaron bajo ambos supuestos con el programa GenAlEx 6.0 (Peakall y Smouse 2006). Para estudiar la relación entre poblaciones se estimó el índice de diversidad genética de Nei (h), (Nei, 1972) y se construyeron dendrogramas usando el algoritmo UPGMA, basados en una matriz de distancias de Nei tanto asumiendo equilibrio Hardy-Weinberg como homocigosis completa. Las matrices de distancia y los dendrogramas fueron obtenidas con el programa POPGENE 1.32 (Yeh y Boyle, 1997).
Con el fin de poder conocer la estructura de la diversidad genética entre y dentro de poblaciones se realizó un Análisis Molecular de Varianza (AMOVA) para obtener un estimador del índice de fijación de Wright (1951), FST (FST). Mediante la prueba de Mantel (Mantel, 1967) se evaluó la hipótesis de aislamiento por distancia como modelo de estructura de poblaciones. Para ello se usó una matriz de distancias geográficas en base a las coordenadas decimales de latitud y longitud de cada sitio de colecta y una matriz de distancias de Nei. Con fines exploratorios, además, se realizó un Análisis de Coordenadas Principales (ACoP) por poblaciones y por individuos. Para estas estimaciones se utilizó el programa GenAlEx 6.0 (Peakall y Smouse, 2006).
]]>
Resultados
Los 12 iniciadores evaluados presentaron entre cinco y 20 bandas amplificadas y de tres a 10 bandas polimórficas. Los cinco iniciadores seleccionados (OPA-11, OPB-06, OPD-03, OPF-06 y OPV-14) mostraron una reproducibilidad de entre 60 y 80 por ciento con un promedio de 13 bandas polimórficas por iniciador (Cuadro 1).
En el estudio de las nueve poblaciones, estos iniciadores amplificaron 71 bandas analizables totales de un tamaño molecular estimado de entre 1933 y 311 pb. En general y tomando en consideración distorsiones en la forma del frente de la corrida electroforética, se consideró que fragmentos con diferencias de hasta un 3% en el tamaño estimado por el programa Cross Checker en diferentes geles podían corresponder a un mismo locus.
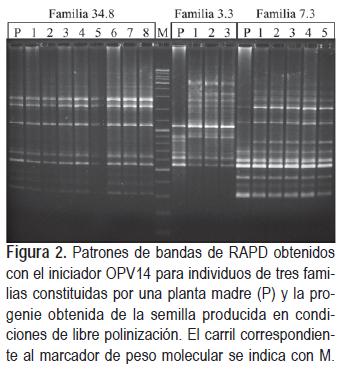
No se observó ninguna variabilidad consistente dentro de las progenies analizadas mientras que cada progenie produjo un patrón de bandas claramente diferente (Figura 2). El resultado del análisis de estos datos arrojó valores de tm de 0,001 con un error estándar menor a 0,0001 tanto para las progenies colectadas en el campo como para las progenies obtenidas de la población con individuos regenerados de poblaciones diferentes.
]]>
Un resumen de la diversidad dentro de las poblaciones estudiadas se presenta en el Cuadro 2. Los valores de P máximo y mínimo variaron entre 46 y 18% respectivamente con una media de 34%. El índice He para las distintas poblaciones varió entre 0,180 y 0,052 con una media de 0,129 bajo el supuesto de equilibrio y entre 0,187 y 0,073 con una media de 0,130 bajo el supuesto de homocigosis. Estos valores muestran un amplio rango de variación entre las poblaciones estudiadas donde la población 6 presentó la mínima diversidad y la población 4 la máxima bajo ambos supuestos.
En el ACoP de los 270 individuos (Figura 3) la Coordenada 1 explica el 26% de la variación total y con la Coordenada 2 ambos ejes acumulan un 45% de la variación. El diagrama muestra a la mayoría de las poblaciones agrupadas aunque los individuos de algunas poblaciones aparecen distribuidos en más de un grupo. En particular, la población 3 se distribuye ampliamente en los dos cuadrantes superiores aunque predomina en el izquierdo (23 individuos), mientras que más concentrada, la población 8 se distribuye en forma opuesta entre los cuadrantes inferiores y predominantemente sobre el derecho (24 individuos). Las poblaciones 1, 9 y 4 se encuentran en su totalidad en un cuadrante diferente cada una. La población 1 es la predominante junto con la mayor parte de la población 8 en el cuadrante inferior derecho. La sección superior derecha reúne a las poblaciones 4; 2 y parte de la 3. Las poblaciones 5; 6 y 7 en su mayoría se concentran en el cuadrante inferior izquierdo.
Existe una diversidad entre poblaciones del 44% y dentro de las poblaciones del 56% (Cuadro 3). El valor de fST de 0,440 fue altamente significativo (p<0,001; 1000 permutaciones). En cuanto a las diferencias entre las poblaciones, el Cuadro 4 resume el índice de la diversidad de Nei (h) y fST. Los valores de h con una media de 0,175 varían entre 0,071 (poblaciones 3 y 6) para las más similares y 0,295 (poblaciones 9 y 1) para las más distantes. Los valores de fST varían entre 0,273 para las poblaciones más cercanas (poblaciones 2 y 3) y 0,593 para las poblaciones más distante (poblaciones 1 y 9) con una media de 0,4395.
En el dendrograma bajo el supuesto de homocigosis total no hay grandes diferencias entre las poblaciones; las poblaciones 1 y 8 aparecen más agrupadas pero distantes entre sí y las poblaciones 3, 6 y 7 se mantienen agrupadas (Figura 4A). Con el supuesto de Equilibrio de Hardy-Weinberg se encuentra la población 1 más distante y las poblaciones 3, 6 y 7 agrupadas (Figura 4 B).
]]>Los primeros tres ejes en el ACoP para las nueve poblaciones explican el 78% de la variación total (Figura 5). Existen algunas poblaciones agrupadas como 3, 5, 6 y 7, y otras aisladas como 1, 2, 4, y 8. La población 8 está separada y muy distante del resto. Las poblaciones 1 y 4 son opuestas y alejadas del núcleo. La población 2 también se encuentra alejada del grupo central pero cercana a la 4.
El resultado obtenido con la prueba de Mantel para las matrices de distancia genética y geográfica muestra que la correlación entre ambas es prácticamente nula (r = 0,0008; p< 0,001; 1000 permutaciones), con una importante dispersión r2 = 0,011 (Figura 6).
Discusión
]]>
El presente trabajo enmarca el primer esfuerzo para estudiar la diversidad genética de S. neesiana con marcadores moleculares. Los valores promedio de reproducibilidad obtenidos son cercanos al 75% logrado en diferentes evaluaciones de reproducibilidad para RAPD (Jones et al., 1997; Penner et al., 1993) lo que indica que se obtuvieron condiciones de confiabilidad esperables para la técnica utilizada.
Sistema reproductivo
En base a los resultados obtenidos, se estima que el porcentaje de autogamia es cercano al 100%, lo que es coincidente con las observaciones de Connor (1979) y Rosengurtt (1946) y con los valores de diversidad (Hamrick y Godt ,1990). Si bien en el muestreo de progenies presentado en este trabajo no se detectó ningún evento de fecundación cruzada, es posible que exista un bajo porcentaje de alogamia que genera variabilidad en las poblaciones. La detección de estos eventos requeriría un muestreo más extenso que el se presenta aquí, sin embargo los resultados obtenidos permiten considerar la especie como altamente autógama.
La riqueza genética puede ser determinada mediante los parámetros de diversidad genética, porcentaje de bandas polimórficas y heterocigosis esperada. El P promedio para las nueve poblaciones estudiadas fue de 34%. Estos valores fueron inferiores a los encontrados con RAPD para otras especies del género Stipa como S. grandis con valores entre 89% (Shan et al., 2006) y 76% (Zhao et al., 2008), S. kriyovii 97% (Wang et al., 2006) y otras gramíneas también alógamas como Poa trivialis 85% (Rajasekar et al., 2006). Los valores obtenidos para S. neesiana son intermedios y congruentes con el rango obtenido por Hamrick y Godt (1990) para pasturas perennes a partir de estudios realizados con isoenzimas (28% y 39%) y similares a los valores para otras gramíneas autógamas como Oryza rufipogon 32% (Ge et al.,1999) con RAPD. El valor de He promedio de las poblaciones estudiadas de 0,13 es menor al hallado con la misma técnica para especies alógamas de Stipa como S. grandis 0,32 (Zhao et al., 2008), S. krylovii 0,162 (Wang, 2006) y 0,226 (Han et al., 2003). Es similar al promedio de 0,12 para ocho especies autógamas (Schoen y Brown, 1991) y superior al 0,09 obtenido por Hamrick y Godt (1990) para siete especies autógamas. En base a estos parámetros, la diversidad intrapoblacional en las poblaciones estudiadas resulta media a alta para especies con el mismo sistema reproductivo y forma de dispersión, lo que deberá ser tomado en cuenta al planificar futuras colecciones de esta especie en Uruguay.
Diversidad interpoblacional
La comparación de la diversidad genética entre las poblaciones estudiadas mediante AMOVA refleja una significativa diversidad. El valor de fST de 0,44 obtenido está indicando una alta variabilidad entre las poblaciones de S. neesiana y se considera como indicador de una importante estructura entre las poblaciones (Heywood 1991), así mismo para Hartl y Clark (1997) los valores de FST superiores a 0,25 reflejan un alto grado de diferenciación entre poblaciones. En la actualidad está claramente establecido que la estructura de las poblaciones de plantas está definida entre otros factores por el sistema reproductivo, flujo de genes (la forma de dispersión del polen, la dispersión y reclutamiento de semillas), deriva, selección y adaptación (Hamrick y Godt, 1990). En comparación con gramíneas perennes con diferentes sistemas reproductivos, S. neesiana presenta una diversidad entre poblaciones superior a especies alógamas del género como S. krylovii, con 36% (Wang et al., 2006), de S. grandis con el 25% (Zhao et al., 2008) y 38% para Sesleria albicans (Reisch, 2003). En un estudio de resultados experimentales de 32 especies autógamas, los valores de FST variaron de entre 0,026 a 0,78. Con un valor promedio de 0,51 (Hamrick y Godt, 1990). Asimismo es coincidente la media de h hallada de 0,13 con los valores encontrados por Schoen y Brown (1991) para ocho especies autógamas usando isoenzimas (máximo 0,294, mínimo 0,008 y una media de 0,125). En el caso de Poa annua, con RAPD, el índice h para 47 poblaciones fue de 0,241 (Mengistu et al., 2000). Los datos obtenidos estarían indicando no sólo la existencia de una importante diversidad entre las poblaciones estudiadas sino que los niveles detectados son típicos de especies autógamas. En las especies en que las semillas representan la principal etapa de traslado, su dispersión es el proceso demográfico preponderante, de modo que influye en la estructura genética (Nathan y Muller-Landau, 2000). Hamrick y Godt (1990) en una revisión de trabajos de diversidad con isoenzimas para 52 especies con dispersión por zoocoría encontraron valores de GST de 0,25. Por otra parte, Green et al. (2001) para un estudio de diversidad con dos niveles de muestreo (predio y país) de Anisantha sterelis, una especie reportada como autógama, encontraron contrastes en la diversidad dentro de los sitios de colecta (FST entre 0,41 a 0,11; media 0,31). Una de las explicaciones propuestas para este fenómeno es un escenario de aumento de las migraciones de larga distancia de las semillas debido a los traslados de maquinaria y de los rastrojos de cosechas para la alimentación del ganado. Vittoz y Engler (2007) establecen que las especies con semillas capaces de adherirse a los animales mayores como ovejas y vacunos pueden dispersarse a grandes distancias, las que se incrementan por los fenómenos de trashumacia en períodos secos.
]]>Gardener et al. (2003) estudiaron los mecanismos de dispersión de S. neesiana concluyendo que el 25% de los frutos se mantenían en la lana luego de cinco meses y cerca del 50% se mantenían viables luego de ser digeridas por el ganado; por otra parte en la dispersión por viento la mayoría de las semillas quedaron a 1 m de la planta madre. Connor et al. (1993) y Bourdôt y Hurrel (1989) estudiando la dispersión de S. neesiana en Nueva Zelanda establecieron que los principales mecanismos son el traslado del ganado y la maquinaria. Si bien los valores de diversidad obtenidos para S. neesiana son levemente superiores a los esperables para especies con estos mecanismos de dispersión, los muestreos realizados no permiten asociar el patrón de distribución de la diversidad de las poblaciones con los traslados de animales requeridos para las sucesivas etapas de cría, recría y engorde. Esto deberá ser considerado en el diseño de futuros trabajos.
Variación geográfica
Los dendrogramas y los análisis de Coordenadas Principales permiten visualizar un conjunto de poblaciones agrupadas aunque diferenciadas entre sí rodeado de un grupo de poblaciones que ocupan posiciones más periféricas en el ordenamiento y que no aparecen agrupadas. Este ordenamiento no pudo ser asociado con factores geográficos o ecológicos por lo que no surge ningún patrón evidente de distribución espacial de la variabilidad genética interpoblacional.
]]>
Para otros modelos de especies herbáceas suficientemente estudiados en Uruguay, se han encontrado diferencias entre las regiones norte y sur en general tanto utilizando marcadores moleculares como en el caso de Turnera sidoides (Speranza et al., 2007) o morfológicos como en el caso de Petunia axillaris (Ando et al., 1994). Estos patrones son congruentes con la información preliminar disponible para S. neesiana (Symonds y Villagrán, 1988). Sin embargo en el presente trabajo, la prueba de Mantel para la escala geográfica estudiada no muestra un nivel de correlación significativa entre las distancias geográficas y genéticas entre poblaciones, como se esperaría bajo un modelo de aislamiento por distancia y como sucede con Stipa capillata cuyas poblaciones del centro de Europa son relictuales con escasa dispersión de polen y semillas (Hensen et al., 2009). Esto puede suceder en los casos en que la distribución de la variabilidad es no lineal, o casos extremos de patrones de variación regulares o alternos (Heywood, 1991). Por otra parte, si la variación observada es el resultado de la selección natural ambientalmente inducida, la similitud entre poblaciones deberá reflejar la similitud entre ambientes, será independiente de la distancia geográfica y no se verá reflejada en la distribución de marcadores genéticos neutros (Volis et al., 2001).
Si bien la caracterización fenotípica de los materiales no fue el objetivo del presente trabajo, se realizaron observaciones morfológicas preliminares en algunos individuos de cada población. Estas observaciones sugieren que la población 9 podría corresponder a la subespecie longiaristata descrita por Arechavaleta (1895). Esta población sin embargo no aparece como genéticamente diferenciada de las demás. La determinación de la diferenciación genética entre entidades infraespecíficas de S. neesiana probablemente requiera de una estrategia de muestreo específicamente diseñada con este propósito.
En conclusión los resultados obtenidos muestran que Stipa neesiana es una especie autógama y que las colecciones disponibles muestran una importante diversidad entre y dentro de poblaciones. Futuras colectas deberían priorizar la cantidad de sitios diferentes al ser éste el factor que más influye sobre la diversidad, incluyendo la representación de un alto número de individuos por población debido a que algunas poblaciones pueden incluir individuos genéticamente muy diferentes entre sí. Se deberían incluir las zonas ausentes, incluso las tradicionalmente consideradas de poco aporte a la diversidad debido a su desarrollo agrícola como los departamentos de Soriano y Colonia, pues nuestros resultados sugieren que pueden contener gran diversidad incluso entre poblaciones cercanas.
Este trabajo forma parte de la Tesis de Maestría en Ciencias Agrarias del primer autor. Este trabajo fue parcialmente financiado por la Comisión Sectorial de Investigación Científica de la Universidad de la República (UdelaR). El primer autor recibió apoyo del programa de Posgrados de la Facultad de Agronomía (UdelaR) y de la Agencia Nacional de Investigación e Innovación. También agradecemos a la Dra. Graciela García y la MSc. Mercedes Rivas por sus aportes como integrantes del tribunal de tesis de Maestría de este trabajo.
Bibliografía
Adler P., Raff D. and Lauenroth W. K. 2001. The Effect of Grazing on the Spatial Heterogeneity of Vegetation. Oecologia; 128 (4): 465-479.
Altesor A., Piñeiro G., Lezama F., Jackson R., Sarasola M. y Paruelo J.M. 2006. Ecosystem Changes Associated with Grazing in Subhumid South American Grasslands. J. Veg. Sci.; 17(3): 323-332.
Ando T., Iida S., Kokubun H., Ueda, Y. and Marchesi E. 1994. Distribution of Infraspecific Taxa of Petunia axillaris (Solanaceae) in Uruguay as Revealed by Discriminant Analyses. Acta Phytotaxon. Geobot.; 45(2): 95-109.
]]>
Arechavaleta J. 1895. Las gramíneas uruguayas. Montevideo: Oriental. 553p.
Arechavaleta J. 1894-97. Las gramíneas uruguayas. Anales del Museo Nacional de Montevideo; 1(1-4): 29-581.
Berretta A., Condón F. y Rivas M. 2007. 2do. informe país sobre el estado de los recursos fitotegenéticos para la alimentación y la agricultura. Montevideo. 114p.
Berreta E.J., Formoso D., Carvajal C.M., Fernández J. y Gabachutto I.R. 1990. Producción y calidad de diferentes especies forrajeras nativas en condiciones de campo. En: II Seminario Nacional de Campo Natural, Tacuarembó. Montevideo: Hemisferio Sur. pp. 49-62.
Boggiano P. 1990. Evaluación de 14 gramíneas perennes bajo pastoreo. En II Seminario Nacional de Campo Natural, Tacuarembó. Montevideo: Hemisferio Sur. pp. 185-195.
]]>
Bourdôt G.W. and Hurrel G.A. 1989. Cover of Stipa neesiana Trin. & Rupr. (Chilean needle grass) on Agricultural and Pastoral Land Near Lake Grassmere, Marlborough. New Zeal. J. Bot.; 27: 415-420.
Bowden W. M. and Senn H.A. 1962.Chromosome Number in 28 Grass Genera from South America. Can. J. Bot.; 40:1115 – 1124.
Buntjer B. J. 2000.CROSSCHECKER: Computer-assisted Scoring of Genetic AFLP Data. En: Plant & Animal Genome VIII Conference, San Diego, CA. Dispinible en: http://www.intlpag.org/pag/8/abstracts/pag8664.html. Consultado: 11 abril 2011.
]]>Burkart A. 1969. Flora ilustrada de Entre Ríos (Argentina) : Parte 2. Buenos Aires: INTA. 551p.
Cingolani A.M., Noy-Meir I., Renison D. D. y Cabido M. 2008. La ganadería extensiva, ¿es compatible con la conservación de la biodiversidad y de los suelos? Ecología Austral; 18:253-271.
Clayton W.D., Vorontsova, M.S., Harman, K.T. and Williamson, H. (2006). GrassBase - The Online World Grass Flora. http://www.kew.org/data/grasses-db.html. Consultado 08 Agosto 2008.
Connor H. E. 1979. Breeding System in the Grasses: a Survey. New Zeal. J. Bot.; 17: 547-574.
Connor H. E., Edgar E. and Bourdôt G. W. 1993. Ecology and Distribution of Naturalized Species of Stipa in New Zeland. New Zel. J. of Agr. Res.; 36: 301-306.
]]>Coughenour M.B. 1991. Spatial Components of Plant-hervibore in Pastoral, Ranch and Native Ungulate Ecosystems. J. Range Manage.; 44: 530-542.
DIEA. 2001. CGA 2000. Programa SICA. Disponible en: http://www.mgap.gub.uy/portal/hgxpp001.aspx?7,5,64. Consultado: agosto 2008.
Doyle J. J. and Doyle J. L. 1987. A Rapid DNA Isolation Procedure for Small Quantities of Fresh Leaf Tissue. Phytochem. Bull.; 19: 11-15.
Frankel O.H., Brown A.H.D. and Burdon J.J. 1995. The Conservation of Plant Biodiversity. Cambridge: Cambridge University Press. 299 p.
Frankel R. and Galun E. 1977. Pollination Mechanisms, Reproduction and Plant Breeding. Berlín: Springer- Verlag. 281p.
]]>García M.A., González O.A. y Queheille F. 2005. Efectos de la fertilización nitrogenada y la intensidad de pastoreo sobre los componentes de la producción de forraje de Stipa setigera Presl. en campo natural (Tesis de grado). Montevideo: Facultad de Agronomía. 168p.
Gardener M.R., Whalley R.D.B. and Sindel B.M. 2003. Ecology of Nassella neesiana, Chilean Needle Grass, in Pastures on the Northern Tablelands of New South Wales: I. Seed production and dispersal. Aust. J. Agr. Res.; 54: 621-626.
Ge S., Oliveira G.C., Schaal B.A., Gao L.Z. and Hong D.Y. 1999. RAPD Variation within and between Natural Populations of the Wild Rice Oryza rufipogon from China and Brazil Heredity; 82:638-644.
Green J.M., Barker J.H.A., Marshall E.J.P., Froud-Williams R.J., Peters N.C.B., Arnold G.M. and Dawson, et al. 2001. Microsatellite Analysis of the Inbreeding Grass weed Barren Brome (Anisantha sterilis) Reveals Genetic Diversity at the within- and between-farm Scales. Mol. Ecol.; 10:1035-1045.
Hamrick J.L. and Godt M.J.W. 1990. Allozyme Diversity in Plant Species. En: Brown A.H.D., Clegg M.T., Kahler A.L. and Weir B.S. (Eds.) Plant Population Genetics, Breeding and Genetic Resources. Massachussets: Sinauer Associates. pp. 43-63.
]]>Han B., Wang J. and Zhao M.L. 2003. Genetic Differentiation of Stipa krylovii in Different Degraded Soil. Acta Agr. Sin.; 2: 146-153.
Hartl D.L. and Clark A.G. 1997. Principles of Population Genetics. 3th. ed. Sunderland: Sinauer Associates. 542 p.
Hensen I., Kilian C., Wagner V., Durka W., Pusch J. and Wesche K. 2009. Low Genetic Variability and Strong Differentiation among Isolated Populations of the Rare Steppe Grass Stipa capillata L. in Central Europe. Plant Biol.; 11: 812-820.
Heun M. and Helentjaris J.P. 1994. Inheritance of RAPDs in F1 Hybrids of Corn. Theor Appl Genet.; 87: 689-696.
Heywood J.S. 1991. Spatial Analysis of Genetic Variation in Plant Populations. Annu. Rev. Ecol. Syst.; 22: 335-55.
]]>Izaguirre P. 1993. Notas en Stipeae I. La región de la corona. Bol.Invest. (Fac. Agron.); (34): 24p.
Jones C.J., Edwards K.J., Castaglione S., Winfield M.O., Sala F., van deWiel, G. et al. 1997. Reproducibility Testing of RAPD, AFLP and SSR Markers in Plants by a Network of European Laboratories. Mol.Breeding; 3: 381-390.
Lacuague L. y Durán V. 1989. Evaluación del rendimiento y calidad de cinco estirpes nativas bajo dos sistemas de corte. (Tesis de grado). Montevideo: Facultad de Agronomía. 661p.
Longhi-Wagner H. M. e Zanin A. 1998. Padrões de distribuição geográfica das espécies de Stipa L. (Poaceae-Stipeae) ocorrentes no Brasil. Rev. Bras. Bot.; 21: 167-175.
Mantel N. 1967. The detection of disease clustering and a generalized regression approach. Cancer Res.; 27: 209-220
]]>
Mengistu L.W., Mueller-Warrant G.W. and Barker R.E. 2000. Genetic Diversity of Poa annua in Western Oregon Grass Seed Crops. Theor. Appl. Genet.; 101: 70-79.
Millot J.C., Methol R. y Risso D. 1987. Relevamiento de pasturas naturales y mejoramientos extensivos en áreas ganaderas del Uruguay: Informe técnico de la Comisión Honoraria del Plan Agropecuario. Montevideo: Consultora F.U.C.R.E.A. 199 p
Nathan R. and Muller-Landau H.C. 2000. Spatial Patterns of Seed Dispersal, their Determinants and Consequences for Recruitment. TREE; 15: 278-285.
]]>Nei M. 1972. Genetic Distance between Population. Am.Nat.; 106: 283-292.
Peakall R. and Smouse P.E. 2006. GENALEX 6: Genetic Analysis in Excel. Population Genetic Software for Teaching and Research. Mol. Ecol. Notes; 6: 288-295.
Penner G.A., Bush A., Wise R., Kim W., Domier L. and Kasha K. et al. 1993. Reproducibility of Random Amplified Polymorphic DNA (RAPD) Analysis among Laboratories. Genome Res. 2: 341-345.
Rajasekar S., Fei S. and Christians N.E. 2006. Analysis of Genetic Diversity in Rough Bluegrass Determined by RAPD. Crop Sci.; 46:162-167.
Ramanatha Rao V. and Hodgkin T. 2002. Genetic Diversity and Conservation and Utilization of Plant Genetic Resources. Plant Cell Tiss. Org.; 68: 1-19.
]]>Reisch C., Poschlod P. and Wingender R. 2003. Genetic Differentiation among Populations of Sesleria albicans Kit. ex Schultes (Poaceae) from Ecologically Different Habitats in Central Europe. Heredity.; 91: 519-527.
Ritland K. and Jain S.K. 1981. A Model for the Estimation of Outcrossing Rate and Gene Frequencies Using n Independent Loci. Heredity; 47: 35-52.
Ritland K. 2002. Extensions of Models for the Estimation of Mating Systems Using n Independent Loci. Heredity; 88: 221-228.
Rivas M. 2001. Sistema reproductivo y estructura genética de poblaciones de Bromus auleticus Trinius ex-Nees (Poaceae): Estudio mediante isoenzimas. Agrociencia; 5: 32- 40.
Rosengurtt B. 1979. Tablas de comportamiento de las especies de plantas de campos naturales del Uruguay. Montevideo: Universidad de la República. 86 p.
]]>Rosengurtt B. 1946. Gramíneas y leguminosas de Juan Jackson; comportamiento en el campo y en el cultivo. En: Estudios sobre praderas naturales del Uruguay. Montevideo. pp. 215 – 346.
Rosengurtt B., Arrillaga de Maffei B.R. e Izaguirre de Artucio P. 1970. Gramíneas Uruguayas. Montevideo: Universidad de la República. 489 p.
Rosengurtt B., Gallinal J.P., Aragone L. y Campal E.F. 1939. La variabilidad de la composición de las praderas. Rev Asoc. Ing. Agr.; 11(3): 28-33.
Shan D., Zhao M.L., Han B. and Han G.D. 2006. Genetic Diversity of Stipa grandis under Different Grazing Pressures. Acta Ecol. Sinica; 26: 3175 – 3183.
Schoen D.J. and Brown A.H.D. 1991. Intraespecific Variation in Population Gene Diversity and Effective Population Size Correlated with Mating System in Plants. Proc. Natl. Acad. Sci.; 88: 4494-4497.
Speranza P.R. 2005. Evolutionary Patterns in the Dilatata Group (Paspalum, Poaceae): a Polyploid/agamic Complex. (Tesis Doctorado) Florida: University of Florida. 119p.
Speranza P. R., Seijo J.G., Grela I. A. and Solís Neffa V. G. 2007 Chloroplast DNA Variation in the Turnera sidoides L. Complex (Turneraceae): Biogeographical Implications. Journal of Biogeography.; 34(3): 427-436.
Symonds G. y Villagrán A. 1988. Pautas para tener en cuenta y comparación de metodologías para elaboración de descriptores, un caso: Stipa setígera Presl. (Tesis de grado). Montevideo: Facultad de Agronomía.
]]>Vittoz P. and Engler R. 2007. Seed Dispersal Distances: a Typology Based on Dispersal Modes and Plant Traits. Bot. Helv.; 117: 109-124.
Volis S., Yakubov B. and Shulgina I. 2001. Tests for Adaptive RAPD Variation in Population Genetic Structure of Wild Barley, Hordeum spontaneum Koch. Biol. J. Linn. Soc; 74: 289-303.
Wang J. L., Zhao N. X., Gai Y. B., Lin F., Ren A. Z., Ruan W. B. and Chen L. 2006. RAPD Analysis of Genetic Diversity and Population Genetic Structure of Stipa krylovii Reshov. in Inner Mongolia Steppe. Genetika; 42: 468-475.
Wildpret de la Torre W., Martín Osorio V.M. y Reyes Betancort J. A. 1999. Nassella neesiana (Trin. & Rupr.) Barkworth, una especie invasora en los espacios naturales protegidos de Canarias. Anuario del Instituto de Estudios Canarios; 44: 35-46.
Williams J.G., Kubelik A.R., Livak K.J., Rafalski L.A. and Tingey S.V. 1990. DNA Polymorphism Amplified by arbitrary Primers are Useful as Genetic Markers. Nucleic Acids Res.; 18: 6531-6535.
]]>Wright S. 1951 The Genetical Structure of Populations. Ann. Eugenics.; 15: 323-354.
Yeh F.C. and Boyle T.J.B. 1997. Population Genetic Analysis of Co-Dominant and Dominant Markers and Quantitative Traits. Belg. J. Bot.; 129: 157.